Luigi Ricciardi 1 , Rosa Mazzeo 2,*©, Angelo Raffaele Marcotrigiano 1 , Guglielmo Rainaldi 3 , Paolo Iovieno 4 , Vito Zonno 1 , Stefano Pavan 1 © an Concetta Lotti 2,*
- 1 Departement fir Buedem, Planz a Liewensmëttel Sciences, Planz Genetik an Zucht Eenheet Universitéit Bari, Via Amendola 165/A, 70125 Bari, Italien; luigi.ricciardi@uniba.it (LR);angelo.marcotrigiano@uniba.it (ARM); vito.zonno@uniba.it (VZ); stefano.pavan@uniba.it (SP)
- 2 Departement vun de Wëssenschaften fir Landwirtschaft, Liewensmëttel an Ëmwelt, Universitéit Foggia, Via Neapel 25, 71122 Foggia, Italien
- 3 Departement fir Biowëssenschaften, Biotechnologien a Biopharmazeutika, Universitéit Bari, Via Orabona 4, 70125 Bari, Italien; guglielmo.rainaldi@uniba.it
- 4 Departement vun Energie Technologies, Bioenergie, Bioraffinaderi a Green Chimie Division, ENEA Trisaia Research Center, SS 106 Ionica, km 419+500, 75026 Rotondella (MT), Italien; paolo.iovieno@enea.it
* Korrespondenz: rosa.mazzeo@unifg.it (RM); concetta.lotti@unifg.it (CL)
mythologesch:
Ënn (Allium cepa L.) ass déi zweet wichtegst Geméiskultur weltwäit a gëtt wäit appréciéiert fir seng gesondheetlech Virdeeler. Trotz senger bedeitender wirtschaftlecher Wichtegkeet a sengem Wäert als funktionell Liewensmëttel, ass d'Zwiebel schlecht ënnersicht mat Respekt fir seng genetesch Diversitéit. Hei hu mir d'genetesch Variatioun am "Acquaviva roude Zwiebel" (ARO) iwwerpréift, eng Landrace mat enger Joerhonnert-aler Kultivatiounsgeschicht an enger klenger Stad an der Provënz Bari (Apulien, Süditalien). E Set vun 11 Mikrosatellitmarker goufe benotzt fir d'genetesch Variatioun an enger Keimplasmasammlung ze entdecken, déi aus 13 ARO Populatiounen an dräi allgemeng kommerziell Aarte besteet. Analysë vun der genetescher Struktur mat parametreschen an net-parametresche Methoden beliicht datt d'ARO e gutt definéierte Genpool duerstellt, kloer ënnerscheet vun den Tropea a Montoro Landracen mat deenen et dacks verwiesselt gëtt. Fir eng Beschreiwung vu Knollen ze bidden, déi normalerweis fir frësche Konsum benotzt ginn, goufe lösleche Feststoffgehalt a Pungenz bewäert, wat méi héich Séissegkeet am ARO mat Respekt fir déi zwee uewe genannte Landrassen weist. Insgesamt ass déi aktuell Etude nëtzlech fir d'Zukunft Valorisatioun vun der ARO, déi duerch Qualitéitslabelen gefördert kënne ginn, déi dozou bäidroe kënnen, kommerziell Bedruch ze limitéieren an d'Akommes vu Klengbesëtzer ze verbesseren.
Aféierung
D'Allium Gattung enthält ongeféier 750 Arten [1], dorënner Zwiebel (Allium cepa L., 2n = 2x =16) ass eng vun de verbreetste. A. cepa huet eng biennial Zyklus an outcrossing reproduktive Verhalen. Hautdesdaags mécht d'Zwiebel weltwäit Produktioun (97.9 Mt) et déi zweet wichtegst Geméiskultur no Tomate [2]. Zënter alen Zäiten sinn Zwiebelknollen souwuel als Liewensmëttel wéi och a Volleksmedizin benotzt. Tatsächlech hunn d'antike Ägypter scho verschidde therapeutesch Formelen gemellt, baséiert op der Notzung vu Knuewel an Zwiebelen an engem medizinesche Papyrus vum 1550 v.
Dëse villsäitege a gesonde Geméis gëtt réi, frësch oder als veraarbechte Produkt konsuméiert a benotzt fir de Goût vu ville Platen ze verbesseren. Verschidde rezent Studien behaapten datt Zwiebelkonsum de Risiko vu kardiovaskuläre Krankheeten reduzéieren kann [4,5], Adipositas [6], Diabetis [7], a verschidde Forme vu Kriibs [8-10]. Zwiebelgesondheetseigenschaften ginn dacks un héije Niveauen vun zwou Klassen vun nutraceutesche Verbindungen zougeschriwwen: Flavonoiden an Alk(en)yl Cysteinsulfoxiden (ACSOs). Déi éischt Klass enthält Flavonolen an Anthocyanine. Quercetin ass den Haaptdetektéierbaren Flavonol, bekannt fir seng staark antioxidant an anti-inflammatoresch Eegeschaften a fräi Radikalen an Iwwergangsmetallionen bindend. [11]; wärend Anthocyanine rout / violett Faarf un e puer Zwiebelzorten ginn. Wat d'ACSOs ugeet, ass déi heefegst Isoalliin [(+)-trans-S-1-propenyl-L-Cysteinsulfoxid] [12], eng net-flüchteg an net-proteinogen Schwefel Aminosäure, déi an den Zellen gespäichert ass, déi indirekt verantwortlech ass fir de schaarfen Aroma a Geschmaach vun Zwiebelen [13]. Beim Tissue Stéierungen gëtt Isoalliin vum Enzym Alliinase gespléckt fir eng Serie vu liichtflüchtege Verbindungen ze produzéieren (Pyruvat, Ammoniak, Thiosulphonaten a propanethial S-Oxid) déi Tréine induzéieren an unangenehmen Geroch verursaachen (Pungency) [14]. D'Zwiebelpungenz gëtt dacks gemooss wéi de Betrag, pro Gramm frësche Gewiicht, vu Pyruvinsäure generéiert duerch Hydrolyse [15.16].
An de Länner vun der Mëttelmier Baseng, proposéiert als ee vun de Secondaire Diversitéit Zentren vun A. cepa [17.18], Zwiebelknollen weisen eng grouss Variabilitéit a Form, Gréisst, Faarf, Trockenstoff a Pungenz [19-22]. Ausserdeem, Schwefel-baséiert Düngung, agronomesch Praktiken, Aart vum Buedem, klimatesch Konditiounen, an de Genotyp vu Kultivarer oder Landrassen kënnen d'Knollenqualitéit beaflossen andeems se komesch organoleptesch an Ernärungswäerter ubidden. [23-27]. An Italien, trotz der breet Ënn Keimplasma Disponibilitéit, sinn nëmmen e puer Zwiebelzorten dacks wëssenschaftlech Studien ënnerworf a richteg charakteriséiert. [28.29].
Eng grëndlech genetesch a phenotypesch Charakteriséierung vun der Agro-Biodiversitéit ass entscheedend fir adequat Konservatioun vu Planzgenetesch Ressourcen ze garantéieren an d'Benotzung vu spezifesche Genotypen an der Wäertkette ze förderen [30-32]. Einfach Sequenzwidderhuelung (SSR) Markéierer goufen dacks fir Kartéierung gewielt [33-35], DNA Fangerofdrock a Kultivar Diskriminatioun [36-38], an zouverlässeg Schätzung vun der genetescher Variabilitéit bannent a tëscht Landrassen [39-42], well se locus spezifesch sinn, multi-allelesch, codominant ierflecher, héich reproduzéierbar a gëeegent fir automatiséiert Genotyping.
An der aktueller Etude hu mir eis Opmierksamkeet op eng traditionell apulesch Landrace konzentréiert, den "Acquaviva roude Zwiebel" (ARO), déi no organesche Landwirtschaftsmethoden an engem klenge Gebitt vun der Stad Acquaviva delle Fonti, an der Provënz Bari kultivéiert gëtt. (Apulien, Süditalien). D'Knollen vun dëser Landrace si grouss a flaach a rout faarweg a gi meeschtens a lokale Rezepter benotzt. Och wann d'ARO d'Qualitéitsmark "Slow Food Presidium" krut, konnt seng Produktioun weider gefördert a geschützt ginn duerch Qualitéitsmarken vun der Europäescher Unioun wéi geschützt geographesch Indikatioun (PGI) a geschützt Hierkonftsbezeechnung (POD), well dës kënnen dozou bäidroen, d kommerziell Bedruch a verbesseren d'Akommes vu Klengbesëtzer. Hei goufen SSR molekulare Markéierer als mächteg Tools benotzt fir genetesch Variatioun tëscht ARO Populatiounen ze bewäerten an dës Landrace vun aneren zwee süd-italienesche Roude Zwiebelen Landracen ze diskriminéieren. Ausserdeem hu mir d'Pungenz an de lösleche festen Inhalt geschätzt fir den ARO Aroma a Relatioun mat der Maartfuerderung ze bewäerten.
Resultater
Etablissement vun Acquaviva Red Onion Germplasma Sammlung a Morphologesch Charakteriséierung
Somen vun 13 Populatiounen vun der ARO Landrace, gespent vu Baueren am Kader vum BiodiverSO Apulia Regioun Projet goufen benotzt fir eng ARO Keimplasma Sammlung opzebauen.
Morphologesch Deskriptoren, am Zesummenhang mat Knollen, Haut a Fleesch goufen op ARO Keimplasma gesammelt an op dräi Zwiebel Landracen, zwee vun der "Tropea roude Zwiebel" (TRO) Landrace an een zu der "Montoro Kupfer Zwiebel" (MCO) Landrace (Figure) 1). All d'ARO Knollen waren flaach a sech duerch rout extern Haut a Fleesch mat verschiddenen Nuancen vun rout charakteriséiert. Am Géigesaz, waren d'Fleesch vun TRO Knollen voll rout, wärend d'Fleesch vun MCO Knollen schlecht pigmentéiert war (Table S1). Biochemesch Analyse erlaabt de festen soluble Inhalt an d'Pungency ze evaluéieren. Wéi an der Tabell gemellt 1, d'Moyenne Wäerter vun fest soluble Inhalt vun Knollen an ARO Populatiounen war 7.60, a gounge vun 6.00 (ARO12) bis 9.50 ° Brix (ARO11 an ARO13). Dëse Wäert war méi héich wéi dee geschätzte fir d'TRO- a MCO-Landracen (4.25 an 6.00° Brix respektiv).

Table 1. Solid Soluble Inhalt a Pungency Wäerter bewäert an "Acquaviva Red Onion" (ARO), "Tropea Red Onion" (TRO), an "Montoro Copper Onion" (MCO) Populatiounen *.
| CODE | Soluble Solid Content (Brix) | Pungency (pmolg-1 FW) | ||
| Mëttelen | CV y (%) | Mëttelen | CV y (%) | |
| ARO 1 | 6.25 D * | 5.65 | 5.84 ab | 23.78 |
| ARO 2 | 7.25 DC | 4.87 | 6.51 ze | 22.98 |
| ARO 3 | 7.50 BCD Eng | 9.42 | 5.28 ab | 22.88 |
| ARO 4 | 7.50 BCD Eng | 0.00 | 6.97 ze | 3.74 |
| ARO 5 | 7.50 BCD Eng | 0.00 | 6.80 ze | 9.68 |
| ARO 6 | 6.25 D | 5.65 | 4.51 ab | 39.18 |
| ARO 7 | 7.25 DC | 4.87 | 5.25 ab | 15.44 |
| ARO 8 | 9.00 AB | 0.00 | 7.04 ze | 3.49 |
| ARO 9 | 8.25 Uhr ABC | 4.28 | 6.84 ze | 0.15 |
| ARO 10 | 7.00 DC | 0.00 | 5.94 ab | 6.57 |
| ARO 11 | 9.50 A | 7.44 | 5.54 ab | 16.43 |
| ARO 12 | 6.00 D | 0.00 | 4.91 ab | 9.70 |
| ARO 13 | 9.50 A | 7.44 | 6.63 ze | 24.93 |
| MCO | 6.00 D | 0.00 | 4.18 ab | 2.66 |
| TRO1 | 4.25 E | 8.31 | 2.80 b | 2.10 |
| TRO2 | 4.25 E | 8.31 | 4.28 ab | 4.79 |
* Mëttel mat der selwechter Buschtawen an grouss oder kleng sinn net statistesch anescht op 0.01P oder 0.05P, respektiv (SNK d'Test). y Variatiounskoeffizient.
Der Moyenne Wäert vun ARO pungency, duerch heescht vun pyruvic Seier Inhalt bewäert, war 6.00, rangéiert vun 4.51 pmol g-1 FW (ARO6) bis 7.04 (ARO8). Dëse Wäert war méi héich wéi dee geschätzte bei TRO a MCO Landrassen (3.54 pmol g-1 FW an 4.18 pmol g-1 FW, respektiv).
SSR Polymorphismus a genetesch Bezéiungen tëscht Zousaz
An der heiteger Etude, 11 vun 37 getest SSR primer Kombinatioune gëtt Single-locus polymorphisms, dh, déi maximal zwee amplification Produiten an engem eenzege Individuum. Insgesamt goufen 55 Allele an 320 Individuen entdeckt mat enger Zuel vun Allele pro Locus, rangéiert vun 2 (ACM147 an ACM 504) bis 11 (ACM132) an engem mëttleren Wäert vu 5 Allele (Tableau) 2). An eenzelne Populatiounen war d'Zuel vun Allele (Na) vun 1.94 (ACM147 an ACM504) bis 5.38 (ACM132), wärend déi effektiv Zuel vun Allele (Ne) vun 1.41 (ACM152) op 2.82 (ACM449) goung. Ënnerscheeder tëscht Na an Ne Wäerter waren wéinst der Präsenz vun alleles mat niddereg Frequenz an de Populatiounen an der predominance vun nëmmen e puer alleles. Den héchsten observéierten Heterozygositéit (Ho) Wäert gouf fir ACM138 an ACM449 (0.62) beliicht, wärend den niddregsten mat ACM152 (0.25) verbonne war. Erwaart Heterozygositéit (He), déi der theoretescher Erwaardung an enger panmiktescher Bevëlkerung entsprécht, rangéiert vun 0.37 (ACM504) bis 0.61 (ACM132, ACM138, an ACM449). De Wright Fixéierungsindex (Fis), huet Wäerter no bei Null (Duerchschnëtt 0.05) fir all Marker ugewisen, wat ähnlech Wäerter tëscht observéierten an erwaarten Heterozygositéitsniveauen ugewisen huet, wéi erwaart fir eng outcrossing Spezies. D'Effizienz vum individuellen SSR Marker am genetesche Fangerofdrock gouf vum polymorphesche Informatiounsinhalt (PIC) Index geschat, mat engem mëttleren Wäert vun 0.48 a rangéiert vun 0.33 (ACM504) bis 0.67 (ACM132). En aneren Effizienzindex, de Shannon Informatiounsindex (I) huet e Mëttelwäert vun 0.84 ugewisen, an ugeholl Wäerter rangéiert vun 0.45 (ACM152) bis 1.20 (ACM132).
Table 2. Polymorphismus Feature vun den 11 SSR Marker benotzt fir Genetesch Diversitéit an ARO, TRO a MCO Populatiounen ze schätzen. Total Unzuel vun Allele (Na), Band Gréisst Range, a Polymorphic Informatiounsinhalt (PIC) Index Bezéie sech op den Total Set vun 320 Individuen, déi an dëser Etude genotypéiert goufen. Unzuel vun Allele (Na), Zuel vun Effektiv Allele (Ne), Observéiert Heterozygositéit (Ho), Erwaart Heterozygositéit (He), Fixatiounsindex (F)is), an dem Shannon säin Informatiounsindex (I) bezéien sech op Mëttelwäerter berechent aus 16 Populatiounen, Jidderee vun 20 Individuen zesummegesat.
| Locus. | Gesamt Na | Gréisst Range (bp) | PIC | Mëttelen | |||||
| Na | Ne | Ho | He | I | Fis | ||||
| ACM 91 | 4 | 189-205 | 0.40 | 2.63 | 1.72 | 0.38 | 0.39 | 0.66 | 0.04 |
| ACM 101 | 4 | 229-241 | 0.52 | 2.94 | 2.37 | 0.53 | 0.56 | 0.92 | 0.06 |
| ACM 132 | 11 | 186-248 | 0.67 | 5.38 | 2.78 | 0.55 | 0.61 | 1.20 | 0.09 |
| ACM 138 | 5 | 242-272 | 0.66 | 3.69 | 2.82 | 0.62 | 0.61 | 1.09 | -0.02 |
| ACM 147 | 2 | 264-266 | 0.37 | 1.94 | 1.83 | 0.44 | 0.44 | 0.62 | -0.01 |
| ACM 152 | 4 | 228-244 | 0.25 | 2.38 | 1.41 | 0.25 | 0.27 | 0.45 | 0.07 |
| ACM 235 | 4 | 286-298 | 0.41 | 2.81 | 1.77 | 0.44 | 0.41 | 0.72 | -0.06 |
| ACM 446 | 6 | 108-120 | 0.56 | 3.50 | 2.48 | 0.49 | 0.58 | 1.01 | 0.16 |
| ACM 449 | 8 | 120-140 | 0.66 | 4.88 | 2.82 | 0.62 | 0.61 | 1.18 | -0.03 |
| ACM 463 | 5 | 202-210 | 0.47 | 3.38 | 1.95 | 0.46 | 0.48 | 0.83 | 0.05 |
| ACM 504 | 2 | 188-192 | 0.33 | 1.94 | 1.64 | 0.30 | 0.37 | 0.54 | 0.20 |
| Mëttelen | 5 | 0.48 | 3.22 | 2.15 | 0.46 | 0.48 | 0.84 | 0.05 |
Ënnert de Populatiounen, ARO3, ARO6, ARO8, ARO10, TRO1, an MCO ugewisen héije Niveau vun genetesch Variatioun (Ho> 0.5), iwwerdeems déi ënnescht Diversitéit an der Bevëlkerung ARO7 observéiert gouf (Ho = 0.27) (Ergänzungstabell S2). Insgesamt hunn all d'Accessiounen Fis Wäerter no bei Null (Fis Moyenne Wäert = 0.054), wéi erwaart ënner zoufälleg mating Konditiounen.
Analyse vun der molekulare Varianz a genetescher Struktur
Hierarchesch Partitionéierung vun der genetescher Variatioun tëscht a bannent Populatiounen gouf vun AMOVA berechent. D'Resultater beliicht eng bedeitend Fraktioun vun der genetescher Variatioun bannent Populatiounen (87%). Variatioun tëscht Populatiounen, 13%, war héich bedeitend (P < 0.001) (Tabelle 3). Pairwise Wäerter vum Fpt Parameter, en Analog vum Wright's Fst Fixéierungsindex, rangéiert vun 0.002 (ARO2 / ARO10) bis 0.468 (ARO7 / TRO2), ware bedeitend (P <0.05), ausser fir néng Pairwise Vergläicher (Ergänzungstabell S3).
Table 3. Analyse vun molekulare Varianz vun 320 Genotypen aus 16 Populatiounen vun Allium cepa L.
| Source | df | Zomm vu Plazen | Varianz Estimatioun | Varianz (%) | Fpt | P |
| Ënner Populatiounen | 15 | 458.63 | 1.16 | 13% | ||
| Bannent Populatiounen | 304 | 2272.99 | 7.50 | 87% | 0.134 | 0.001 |
| Ganzen | 319 | 2731.62 | 8.66 |
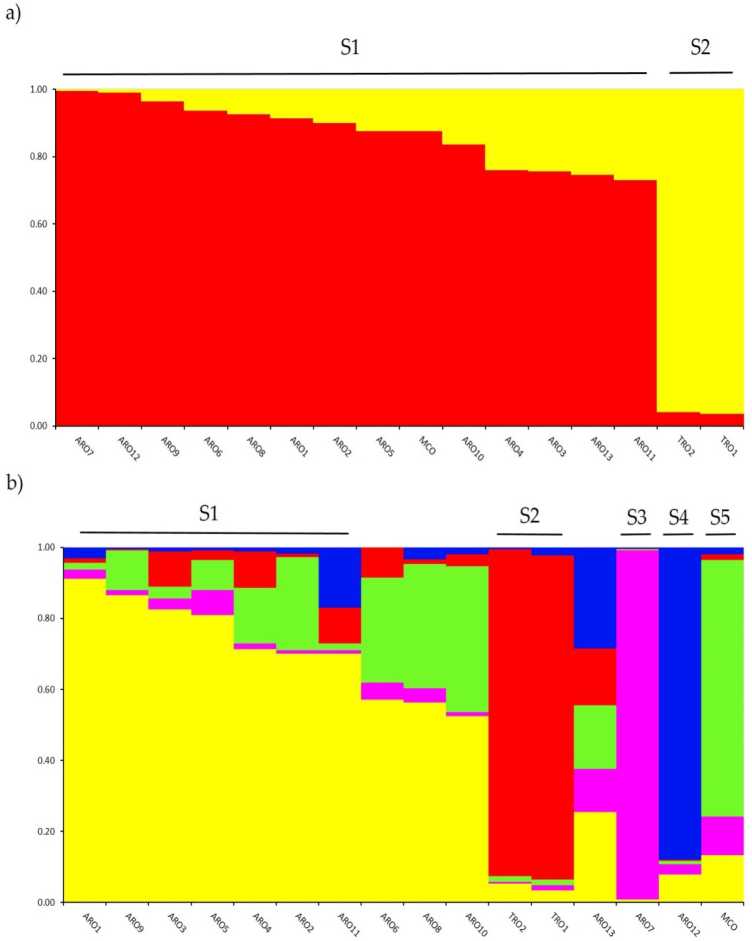
Untersuchung vun der genetescher Struktur an der A. cepa Kollektioun genotyped an dëser Etude war vun heescht vun der admixture Modell-baséiert Clustering Analyse an der Software STRUCTURE ëmgesat. D'Evanno AK Method proposéiert Ënnerdeelung an zwee Stärekéip (K = 2) als déi informativst fir eis Datebank,mam the nächst héchste peak op K = 5 (Supplementaiv Rgure S1). A Forschett = 2, ahpopuerg wier assigned zu onan derf déi zwee Cluster mat a rnernbertoip Koeffizient (q) > 0.7. Wéi shown an Zuelen 2a, den éischte Stärekoup (genannt S1) abegraff MCO an all ARO Populatiounen, iwwerdeems de S2 Stärekoup déi zwee TRO Populatiounen gruppéiere. Bei K = 5, bitt eng méi déif Beschreiwung vum Dataset (Figur 2b), 75% vun de Bäitrëtter goufen zu engem vun de fënnef Stärekoup zougewisen. Trennung tëscht ARO (S1) an TRO (S2) gouf bestätegt, obwuel e puer ARO Populatiounen admixed goufen (q <0.7) oder separat an déi zwee nei Stärekéip S3 an S4 (ARO7 an ARO12, bzw.). Interessanterweis huet de MCO kommerziellen Typ e markante Stärekoup (S5) geformt, getrennt vun der Apulescher roude Zwiebel.
Genetesch Bezéiungen tëscht Populatiounen
SSR Polymorphismus erlaabt en Dendrogramm vun der genetescher Diversitéit ze zéien an d'Resultater vun der phylogenetescher Analyse ginn an der Figur gewisen. 3a. Hei gouf d'Keimplasmasammlung a fënnef Gruppen opgedeelt, staark ënnerstëtzt vu Bootstrap Wäerter. D'ARO7 an d'ARO12 Populatiounen goufen direkt vun de verbleiwen Populatiounen getrennt an hunn zwee verschidde Cluster geformt. Déi drëtt Stärekoup abegraff déi zwou kommerziell Populatiounen vun TRO, Tëschenzäit de véierte Node MCO vun eelef ARO Populatiounen ënnerdeelt. Genetesch Bezéiung, déi tëscht Populatiounen optrieden, gouf weider ënnersicht mat Hëllef vun der Haaptkoordinatanalyse (PCoA) (Figure) 3b). Wéi virdru beliicht, goufen ARO Populatiounen enk gruppéiert, ausser ARO12 an ARO7, déi an isoléierte Positiounen am PCoA Komplott erschéngen. Déi zwee TROs an d'MCO Populatiounen goufen am ënneschten-riets Panel vum Komplott verspreet.
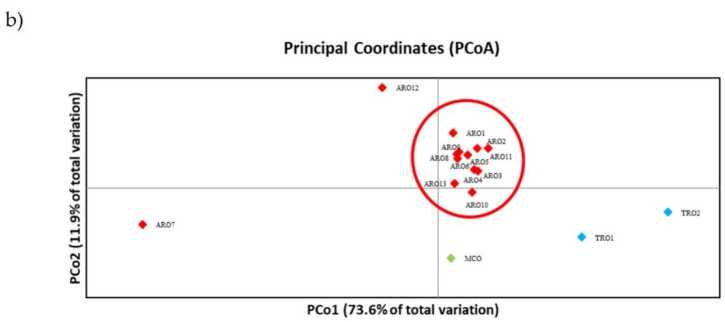
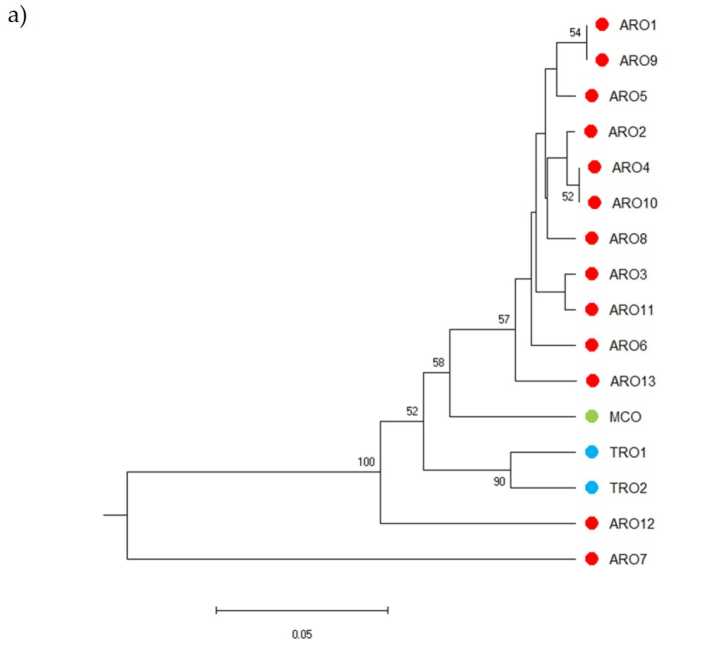
Figure 3. Genetesch Diversitéit tëscht 16 A. cepa Populatiounen an dëser Etude charakteriséiert, baséiert op hirem SSR Profil. (a) UPGMA Dendrogramm vun der genetescher Distanz. Bootstrap Support Wäerter> 50 sinn iwwer déi entspriechend Wirbelen uginn; (b) Haaptkomponentanalyse (PCoA). De Stärekoup ëmkreest a rout voll reagéiert mat der Grupp generéiert duerch phylogenetesch Analyse a besteet aus 11 ARO Bäitrëtter.
Diskussioun
Bannent der grousser Quantitéit vun der Agro-Biodiversitéit, déi traditionell am Süditalien kultivéiert gëtt, representéieren d'Zwiebellandrassen Nischeprodukter, déi aus dem Risiko vun der genetescher Erosioun an der Bedrohung vum Ersatz duerch modern Zorten erhale musse ginn. Am Kader vum regionale Projet BiodiverSO, fir d'Sammelen, d'charakteriséieren, d'Promotioun an d'Sécherheet vun genetesch Ressourcen vun der Apulien Regioun staark verbonne mat lokal Patrimoine, hu mir eng Sammlung vun Somen vun 13 Populatiounen vun der ARO Landrace etabléiert. Mir hunn déi éischt Bewäertung vun der ARO Variatioun a punkto DNA Polymorphismen an zwee biochemesche Parameter gemellt, soluble festen a pyruvinsäure Inhalter, am Zesummenhang mat Goûteigenschaften a vu Wichtegkeet fir d'Akzeptanz vun de frësche ongekachte Produkter. Zousätzlech goufen d'Donnéeën iwwer d'ARO-Landrace verglach mat deenen, déi op zwee aner pigmentéiert Zwiebel-Landracen gesammelt goufen, mat deenen se sech dacks verwiesselt hunn.
Biochemesch Analysen hunn d'Séissegkeet vun den 13 ARO Populatiounen beliicht, am Zesummenhang mat héije lösleche Feststoffgehalt a mëttlerer Pungency, laut de Séiss Zwiebelindustrie Richtlinnen [31]. ARO Knollen ware méi séiss wéi déi vun den TRO- a MCO-Landracen, an hunn e bësse méi héich Pungency gewisen. Wéi och ëmmer, Séissegkeeten an Zwiebelen ass wéinst engem Gläichgewiicht tëscht Zockergehalt a Pungenz, dofir kéint dës Charakteriséierung nëtzlech sinn fir d'Auswiel vu Wäertgenotypen z'ënnerstëtzen, normalerweis vu Baueren nëmmen op Basis vun der Morphologie duerchgefouert.
SSR Markéierer goufen als nëtzlecht Instrument bestätegt fir Genotypen ze ënnerscheeden, och wann se an engem schmuele wuessende Gebitt gesammelt goufen wéi d'Stad Acquaviva delle Fonti. Déi gewielte Marker hunn eng méi héich Unzuel vun Allele gewisen wéi d'Marker virdru gemellt [43] an [44], awer méi niddereg wéi d'Markéierer gemellt vun [45]. Ausserdeem hunn 50% vun eisem Set vu Markéierer PIC Index Wäerter méi wéi 0.5 gewisen, wat sech als gëeegent beweist fir d'Populatiounen an der Sammlung ze diskriminéieren, wéi proposéiert vum [46]. Bewäertung vun Diversitéit bannent Populatiounen verroden ähnlech Wäerter tëscht Ho an He, doraus zu niddereg Fis Wäerter. Dëst ass am Aklang mat der eraus Kräizung Natur vun A. cepa, déi eescht un der Inzuchtdepressioun leiden [47]. Gesamt Fis Wäert berechent an Zwiebelpopulatiounen, déi an dëser Etude considéréiert goufen (0.054) war méi niddereg wéi dee virdru gemellt. [45] (0.22) a bal identesch mat deem fonnt vun [31] (0.08) an [48] (0.00) déi genetesch Diversitéit an Zwiebellandrassen aus Nordweste vu Spuenien an Niger bewäert hunn. Bemierkbar Niveaue vun der Heterozygositéit an ARO Populatiounen verstäerken d'Notioun datt Apulien en Diversitéitszentrum fir vill horticultural Arten duerstellt [32, 42, 49-51].
AMOVA beliicht datt déi meescht molekulare Variatioun an der Sammlung, déi an dëser Etude genotyp ass, bannent de Populatiounen läit. Wéi och ëmmer, bedeitend genetesch Differenzéierung tëscht Populatiounen (FPT Wäerter) huet d'Optriede vun der genetescher Stratifikatioun opgedeckt. Tatsächlech, obwuel eis Resultater d'Präsenz vun der genetescher Uniformitéit an de meeschte ARO Populatiounen uginn, e gutt definéierte Stärekoup bilden, hunn d'ARO7 an ARO12 Populatiounen e kloer z'ënnerscheedde genetesche Profil ugewisen. Dëst Resultat kéint wéinst engem aneren Hierkonft vu Somen sinn, déi vun den zwee Baueren benotzt goufen, aus deenen d'Populatiounen gesammelt goufen. Ausserdeem, baséiert op de kritt Resultater, kann d'ARO Landrace kloer ënnerscheeden op geneteschem Niveau vun den TRO an MCO Landracen ugesi ginn. An enger rezenter Etude, [29] bewäert d'genetesch Diversitéit vu verschiddenen italienesche Zwiebelen, dorënner "Acquaviva", "Tropea" a "Montoro." Och wann d'Autoren SNP Marker benotzt hunn fir d'genetesch Diversitéit vun enger méi breeder Zwiebelsammlung ze bewäerten, konnt d'Genotyping net "Acquaviva" vun "Tropea" an "Montoro" Zwiebelen ënnerscheeden. Wahrscheinlech ass dës Diskrepanz wéinst dem nidderegen duerchschnëttleche PIC-Wäert fonnt (0.292), wat suggeréiert eng bescheiden allgemeng Informativitéit vun de Loci ënner Analyse wéi behaapt vun [29]. Ausserdeem, fir d'Präsenz vun der Ënnerstruktur an hirem italienesche Stärekoup z'ënnersichen, wier et besser gewiescht, déi italienesch Genotypen separat vum Rescht vun der Sammlung ze analyséieren. Wahrscheinlech hätt et erlaabt Muster vun der genetescher Diversitéit ze visualiséieren verbonne mat geographescher Stratifikatioun oder Spuren ënner empirescher Selektioun.
Als Conclusioun duerstellt déi heiteg Etude e komplette Bericht iwwer eng Zwiebellandrace, déi mam lokale kulturelle Patrimoine verbonnen ass a vu wirtschaftlecher Wichtegkeet fir d'Baueren. Eis Resultater ënnersträichen datt, mat e puer Ausnahmen, ARO duerch e gutt definéierte Genpool charakteriséiert ass, dee verdéngt aus dem Risiko vun der genetescher Erosioun ze konservéieren. Dofir war d'Grënnung vun enger representativer Sammlung vun dëser wäertvoller Quell vun der genetescher Diversitéit entscheedend. Schlussendlech kann d'genetesch a phänotypesch Charakteriséierung vun ARO nëtzlech sinn fir Qualitéitszeechen vun der Europäescher Unioun ze kréien.
Materialien an Methoden
Germplasma Sammlung, Planzmaterial, an DNA Extraktioun
Eng Rei vun 13 Populatiounen vun der ARO Landrace goufen am Kader vun engem Apulia Regioun Projet kaaft (BiodiverSO: https://www.biodiversitapuglia.it/), duerch eng Serie vu Missiounen, déi an der "Acquaviva delle Fonti" duerchgefouert goufen, eng kleng apulesch Stad an der Provënz Bari, Italien. Sammlungsplaze vun all Bäitrëtter goufen duerch de Geographic Information System (GIS) kartéiert an an der Tabell gemellt 4. Ausserdeem goufen zwou Populatiounen aus der TRO Landrace an eng Populatioun aus der MCO Landrace an der heiteger Etude abegraff an als Referenze benotzt. All d'Planzmaterial gouf an de selwechte Ëmweltbedéngungen um experimentellen Bauerenhaff "P Martucci" vun der Universitéit vu Bari (41° 1'22.08″ N, 16°54'25.95″ E) ugebaut, ënner Schutzkäfeg fir Kräizpollinatioun tëscht Populatiounen an d'Intra-Bevëlkerungspollinatioun mat Hëllef vu Blowflies assuréieren (Lucilia Caesar). Déi 16 Populatiounen goufen charakteriséiert fir Eegeschaften am Zesummenhang mat der Knollengréisst a Form a Haut a Fleeschfaarf (Table S1). Zousätzlech gouf zolidd soluble Inhalt Assay mat engem handgehalene Refraktometer ausgeführt an d'Pungenz gouf an Zwiebeljus Proben gemooss mat 2,4-dinitrophenylhydrazin (0.125%) v/v an 2N HCl) an d'Evaluatioun vun der Absorptioun bei 420 nm, wéi gemellt vun [31]. Den Duncan Multiple Range Test an den SNK Test goufen duerchgefouert fir d'Präsenz vu wesentlechen Differenzen ze bestëmmen.
Table 4. Lëscht vun Populatiounen gesammelt a genotyped an dëser Etude. Fir all Bevëlkerung, Identifikatiounscode, Lokalen Numm, GPS Koordinat, a Genbank, déi d'Somen erhaalen ginn gemellt.
| Code | Numm | GPS Koordinaten | Gene Bank y |
| ARO 1 | Cipolla rossa di Acquaviva | 40°54’21.708″ N 16°49’1.631” E | Di.SSPA |
| ARO 2 | Cipolla rossa di Acquaviva | 40°53’14.28″ N 16°48’56.879” E | Di.SSPA |
| ARO 3 | Cipolla rossa di Acquaviva | 40°54’11.304″ N 16°49’13.079” E | Di.SSPA |
| ARO 4 | Cipolla rossa di Acquaviva | 40°54’3.348″ N 16°40’27.011” E | Di.SSPA |
| ARO 5 | Cipolla rossa di Acquaviva | 40°51’59.76″ N 16°53’0.527” E | Di.SSPA |
| ARO 6 | Cipolla rossa di Acquaviva | 40°52’48.72″ N 16°49’43.247” E | Di.SSPA |
| ARO 7 | Cipolla rossa di Acquaviva | 40°53’13.47″ N 16°50’23.783” E | Di.SSPA |
| ARO 8 | Cipolla rossa di Acquaviva | 40°53’18.816″ N 16°49’33.888” E | Di.SSPA |
| ARO 9 | Cipolla rossa di Acquaviva | 40°54"51.372" N 16°49"3.504" E | Di.SSPA |
| ARO 10 | Cipolla rossa di Acquaviva | 40°54’1.188″ N 16°49’24.311” E | Di.SSPA |
| ARO 11 | Cipolla rossa di Acquaviva | 40°52"49.8" N 16°49"48.575" E | Di.SSPA |
| ARO 12 | Cipolla rossa di Acquaviva | 40°52’38.892″ N 16°49’28.379” E | Di.SSPA |
| ARO 13 | Cipolla rossa di Acquaviva | 40°53’21.768″ N 16°49’29.711” E | Di.SSPA |
| TRO1 | Cipolla rossa lunga di Tropea | - | Di.SSPA |
| TRO2 | Cipolla rossa tonda di Tropea | - | Di.SSPA |
| MCO | Cipolla ramata di Montoro | - | Di.SSPA |
| y Di.SSPA, Department of Soil, Plant and Food Sciences, University of Bari. |
Leaf Material vun 20 genotypes pro Bevëlkerung goufen Echantillon a bei -80 ° C bis benotzen gespäichert. Fir polysaccharide-räich Arten, wéi A. cepa, Déi éischt Schrëtt fir Polysacchariden ze läschen sinn essentiell fir gutt-Qualitéit DNA ze kréien, dofir goufen initial Wäschungen am STE Puffer (0.25 M Saccharose, 0.03 M Tris, 0.05 M EDTA) gemaach wéi beschriwwen vum [52]. Total DNA gouf no der CTAB Method extrahéiert [53] a schlussendlech gouf et duerch Nano Drop 2000 UV-vis Spektrofotometer (ThermoScientific, Waltham, MA, USA) an 0.8% Agarosegel Elektrophorese fir Qualitéit a Konzentratioun gepréift.
SSR Analyse
16 EST-SSR primer Kombinatioune entwéckelt vun [54] a virdrun an genetesch Diversitéit Studien getest vun [43] an [44] an 21 genomesch SSR [45-55] goufen gepréift fir hir Eegenheet ze evaluéieren (Ergänzungstabell S4). Genotyping gouf mat der wirtschaftlecher fluoreszenter Tagging Method gemaach, an där de M13 Schwanz un all Forward SSR Primer bäigefüügt gëtt [56]. PCR Mëschunge goufen an 20 gL Reaktioun virbereet mat: 50 ng Gesamt DNA, 0.2 mM dNTP Mëschung, 1X PCR Reaktiounsbuffer, 0.8 U DreamTaq DNA Polymerase (Thermo Scientific, Waltham, MA, USA), 0.16 gM Reverse Primer , 0.032 gM vun Forward Primer verlängert mat der M13 Haaptrei (5'-TGTAAAACGACGGCCAGT-3'), an 0.08 gM vun engem universal M13 primer mat FAM oder NED fluorescent Faarfstoffer markéiert (Sigma-Aldrich, St. Louis, MO, USA). D'PCR-Reaktiounen goufen am SimpliAmp (Applied Biosystems, CA, USA) Thermocycler duerchgefouert mat de folgende Konditioune fir d'Majoritéit vun de Primerpairen: 94 ° C fir 5 min, 40 Zyklen bei 94 ° C fir 30 s, 58 ° C fir 45 s an 72 ° C fir 45 s an eng final elongation bei 72 ° C fir 5 min. Wéi fir ACM446 an ACM449, war en Touchdown PCR mat annealing vun 60 ° C bis 55 ° C iwwer 10 Zyklen applizéiert, 30 Zyklen bei 55 ° C, gefollegt vun enger definitiver Verlängerung vu 5 min bei 72 ° C. PCR Produkter goufen an eng 96-Well Plack gelueden a gemëscht mat 14 gL Hi-Di Formamid (Life Technologies, Carlsbad, CA, USA) an 0.5 gL GeneScan 500 ROX Gréisst Standard (Life Technologies, Carlsbad, CA, USA). Amplicons goufen duerch ABI PRISM 3100 Avant Genetic Analyzer (Life Technologies, Carlsbad, CA, USA) Kapillar Sequenzéierungsmaschinn geléist, wou d'Allelen als Co-dominant gezeechent goufen an duerch d'GeneMapper Software Version 3.7 zougewisen ginn.
D'Software GenAlEx 6.5 [57] an Cervus 3.0.7 [58] goufen benotzt fir d'Zuel vun den Allele (Na), d'Zuel vun den effektiven Allele (Ne), observéiert Heterozygositéit (Ho), erwaart Heterozygositéit (He), polymorpheschen Informatiounsinhalt (PIC), Shannon Informatiounsindex (I), a Fixéierungsindex (Fis) ze schätzen. ) fir all SSR Locus.
Bewäertung vun der genetescher Diversitéit
Hierarchesch Partitionéierung vun der genetescher Variatioun tëscht a bannent den Zwiebelpopulatiounen gouf vum GenAlEx 6.5 bewäert. [57] duerch d'Analyse vun der molekulare Varianz (AMOVA) mat 999 Bootstrapping fir Bedeitung ze testen. Ausserdeem gouf GenAlEx 6.5 Software benotzt fir d'Diversitéit an all Populatioun ze schätzen andeems d'Moyenne vun Ho, He, a Fis iwwer all SSR Loci berechnen.
D'Bevëlkerungsstruktur gouf ofgeleet vum Bayesian Modell-baséierte Clustering Algorithmus, implementéiert an der STRUCTURE v.2.3.4 Software [59]. D'Datebank gouf mat enger Zuel vun hypotheteschen Stärekéip (K) gelaf, rangéiert vun 1 bis 10, a setzt zéng onofhängeg Lafen pro all K Wäert. Fir all Laf, fir d'Konsistenz vun de Resultater z'iwwerpréiwen, goufen 100,000 initial Verbrennungsperiod an 100,000 Markov Chain Monte Carlo (MCMC) Iteratiounen ënner dem Zousatzmodell an onofhängege Allelefrequenzen tëscht Populatiounen ausgefouert. De stäerkste wahrscheinlech K-Wäert gouf bestëmmt duerch Ëmsetzung vun der AK Method, beschriwwen vun [60], am web-baséierte Programm STRUCTURE HARVESTER [61]. Eng individuell Bevëlkerung gouf zu engem spezifesche Stärekoup zougewisen wann säi Memberskoeffizient (q-Wäert) méi héich war wéi 0.7, soss gouf et als gemengt Virfahren ugesinn.
Principal Koordinate Analyse war gesuergt Mustere vun genetesch Relatioun tëscht Bäitrëttslänner ze visualiséieren vun der Nei d'genetesch Distanz Matrixentgasung (Ergänzlech Table S5). Baséierend op Allele Frequenzen, gouf en Dendrogramm vun der genetescher Distanz konstruéiert andeems d'ongewiicht Pair Grupp Method mat arithmeteschen Duerchschnëtt (UPGMA) Cluster Analyse an der POPTREEW Software implementéiert [62]. Bootstrapping gouf applizéiert fir d'Vertrauen an hierarchesche Clustering ze bewäerten, 100 Resampling vum Dateset ze setzen. Endlech, MEGA X Software [63] gouf als Bam Zeechnen Software benotzt.
Ergänzungsmaterial: Déi folgend sinn online verfügbar op http://www.mdpi.com/2223-7747/9/2/260/s1. Table S1: Morphologesch Charakteriséierung vun ARO, MCO an TRO Knollen. Dësch S2: Heterozygositéit a Fixéierungsindizes berechent fir ARO Landracen an TRO a MCO Landracen. Dësch S3: Pairwise Wäerter vum Fpt Parameter. Dësch S4: Lëscht vun de SSRs an der Etude benotzt. Dësch S5. Pairwise Populatioun Matrixentgasung vun Nei genetesch Distanz. Figur S1: Zeildiagramm vu K Wäerter verännert mam Evanno's Delta K.
Autor Contributions: CL an LR konzipéiert d'Etude an entworf den Experiment; CL an PI gemaach molekulare Marker Analyse; ARM a VZ hunn d'Feldverspriechen gemaach; RM, SP, GR, an CL waren an Daten Analyse involvéiert; RM an CL hunn d'Manuskript geschriwwen. All Autoren hunn déi publizéiert Versioun vum Manuskript gelies an ausgemaach.
Finanzéierung: Dës Aarbecht gouf finanzéiert vum regionalen apulesche Projet "Biodiversitéit vun apulesche Geméisspezialitéiten" - Programma di Sviluppo Rurale per la Puglia 2014-2020. Misura 10-Sottomisura 10.2; Bewëllegung CUP H92C15000270002, Italien.
Merci geet: Unerkennung ass wéinst "Azienda Agricola Iannone Anna" an "Associazione produttori della vera cipolla rossa di Acquaviva" fir Planzmaterialien ze liwweren, déi am Experiment benotzt ginn.
Conflicts of Interest: D'Auteuren deklaréieren net e Konflikt vun Interesse.
Referenze
- 1. Stearn, WT Wéi vill Arten vun Allium sinn bekannt? Kee Mag. 1992, 9, 180-182. [CrossRef]
- 2. FAOSTAT. FAO Statistesch Datebank. Online verfügbar: http://www.fao.org/2017 (zougänglech den 8. Januar 2019).
- 3. Block, E. D'Chimie vu Knuewel an Zwiebel. Sci. Am. 1985, 252, 114-119. [CrossRef]
- 4. Lee, B.; Jung, JH; Kim, HS Bewäertung vu roude Zwiebel op Antioxidant Aktivitéit bei Rat. Food Chem. Toxicol. 2012, 50, 3912-3919. [CrossRef]
- 5. Lee, SM; Mond, J.; Chung, JH; Cha, YJ; Shin, MJ Effekt vu quercetin-räiche Zwiebelschielen Extrakten op arteriell Thrombose bei Ratten. Food Chem. Toxicol. 2013, 57, 99-105. [CrossRef] [PubMed]
- 6. Yoshinari, O.; Shiojima, Y.; Igarashi, K. Anti-Obesitéit Effekter vum Zwiebelextrakt an Zucker Diabetesch Fett Ratten. Nährstoffe 2012, 4,1518-1526. [CrossRef]
- 7. Akash, MSH; Rehman, K.; Chen, S. Gewierzplanz Allium cepa: Nahrungsergänzung fir d'Behandlung vum Typ 2 Diabetis mellitus. Ernährung 2014, 30, 1128-1137. [CrossRef] [PubMed]
- 8. Wang, Y.; Tian, WX; Ma, XF Inhibitoresch Effekter vun Zwiebel (Allium cepa L.) Extrait op Verbreedung vu Kriibszellen an Adipozyten iwwer d'Inhibitioun vu Fettsäuresynthase. Asiatesch Pac. J. Kriibs Prev. 2012,13, 5573-5579. [CrossRef] [PubMed]
- 9. Lai, WW; Hsu, SC; Chueh, FS; Chen, JJ; Yang, JS; Lin, JP; Lien, JC; Tsai, CH; Chung, JG Quercetin hemmt d'Migratioun an d'Invasioun vu SAS mënschlech mëndlech Kriibszellen duerch Inhibitioun vun NF-kappaB a Matrix Metalloproteinase-2/-9 Signalweeër. Anticancer Res. 2013, 33, 1941-1950. [PubMed]
- 10. Nicastro, HL; Ross, SA; Milner, JA Knuewel an Zwiebelen: Hir Kriibspräventiounseigenschaften. Kriibs Prev. Res. 2015, 8,181-189. [CrossRef]
- 11. Forte, L.; Torricelli, P.; Boanini, E.; Gazzano, M.; Rubini, K.; Fini, M.; Bigi, A. Antioxidant a Knochenreparatiounseigenschaften vu quercetin-funktionaliséierter Hydroxyapatit: Eng In vitro Osteoblast-Osteoklast-Endothelial Zell Co-Kulturstudie. Acta Biomater. 2016, 32, 298-308. [CrossRef]
- 12. Yamazaki, Y.; Iwasaki, K.; Mikami, M.; Yagihashi, A. Verdeelung vun eelef Aroma Virgänger, S-Alk(en)yl-L-Cystein-Derivate, a siwen Allium Geméis. Liewensmëttel Sci. Technol. Res. 2011, 17, 55-62. [CrossRef]
- 13. Block, E. D'Organosulfurchemie vun der Gattung Allium - Implikatioune fir d'organesch Chimie vum Schwefel. Angew. Chem. Int. Ed. Eng. 1992, 31, 1135-1178. [CrossRef]
- 14. Griffiths, G.; Trueman, L.; Crowther, T.; Thomas, B.; Smith, B. Onions-E globale Virdeel fir d'Gesondheet. Phytother. Res. 2002,16, 603-615. [CrossRef]
- 15. Schwimmer, S.; Weston, WJ Enzymatesch Entwécklung vu Pyruvinsäure am Zwiebel als Mooss vu Pungency. J. Agric. Food Chem. 1961, 9, 301-304. [CrossRef]
- 16. Ketter, CAT; Randle, WM Pungency Bewäertung an Zwiebel. An Getest Studien fir Laborunterricht; Karcher, SJ, Ed.; Association fir Biologie Laboratoire Education (ABLE): New York, NY, USA, 1998; Band 19, S. 177-196.
- 17. Hanelt, P. Taxonomie, Evolutioun a Geschicht. An Zwiebelen an Alliéierten Crops, Vol. I. Botanik, Physiologie a Genetik; Rabinowitch, HD, Brewster, JL, Eds.; CRC Press: Boca Raton, FL, USA, 1990; S. 1-26.
- 18. Rabinowitch, HD; Curra, L. Allium Crop Science: Rezent Fortschrëtter; CABI Publishing: Wallingford, UK, 2002.
- 19. Mallor, C.; Carravedo, M.; Estopanan, G.; Mallor, F. Charakteriséierung vun genetesch Ressourcen vun Zwiebel (Allium cepa L.) vum spuenesche Secondaire Zentrum vun Diversitéit. Spann. J. Agric. Res. 2011, 9, 144-155. [CrossRef]
- 20. Ferioli, F.; D'Antuono, LF Evaluatioun vun phenolics an cysteine sulfoxides am lokal Ënn a Schalotten Keimplasma aus Italien an Ukraine. Genet. Ressource. Crop Evol. 2016, 63, 601-614. [CrossRef]
- 21. Petropoulos, SA; Fernandes, A.; Barros, L.; Ferreira, ICFR; Ntatsi, G. Morphologesch, Ernährungs- a chemesch Beschreiwung vu 'vatikiotiko', eng Ënn lokal Landrace aus Griicheland. Food Chem. 2015,182, 156-163. [CrossRef]
- 22. Liguori, L.; Adiletta, G.; Nazzaro, F.; Fratinni, F.; Di Matteo, M.; Albanese, D. Biochemesch, antioxidant Eegeschaften an antimikrobieller Aktivitéit vu verschiddene Zwiebelvarianten am Mëttelmierraum. J. Iessen Meas. Charakter. 2019,13, 1232-1241. [CrossRef]
- 23. Yoo, KS; Pike, L.; Crosby, K.; Jones, R.; Leskovar, D. Differenzen an der Zwiebelpungenz wéinst Kultiveren, Wuesstumsëmfeld a Knollengréissten. Sci. Hortic. 2006,110, 144-149. [CrossRef]
- 24. Beesk, N.; Perner, H.; Schwarz, D.; Georg, E.; Kroch, LW; Rohn, S. Verdeelung vu Quercetin-3, 4'-O-diglucoside, Quercetin-4'-O-monoglucoside, a Quercetin a verschiddenen Deeler vun der Zwiebelbulb (Allium cepa L.) beaflosst vum Genotyp. Food Chem. 2010,122, 566-571. [CrossRef]
- 25. Caruso, G.; Conti, S.; Villari, G.; Borrelli, C.; Melchionna, G.; Minutolo, M.; Russo, G.; Amalfitano, C. Effekter vun der Transplantatiounszäit an der Planzedicht op d'Ausbezuelung, d'Qualitéit an den Antioxidantgehalt vun der Zwiebel (Allium cepa L.) a Süditalien. Sci. Hortic. 2014,166, 111-120. [CrossRef]
- 26. Perez-Gregorio, MR; Regueiro, J.; Simal-Gandara, J.; Rodrigues, AS; Almeida, DPF D'Erhéijung vum Plus vun Zwiebelen als Quell vun antioxidant Flavonoiden: Eng kritesch Iwwerpréiwung. Crit. Rev. Liewensmëttel Sci. Nutr. 2014, 54,1050-1062. [CrossRef] [PubMed]
- 27. Pohnl, T.; Schweiggert, RM; Carle, R. Impakt vun der Kultivatiounsmethod a Kultivarauswiel op löslech Kuelenhydrater a schaarf Prinzipien an Zwiebelen (Allium cepa L.). J. Agric. Food Chem. 2018, 66, 12827-12835. [CrossRef] [PubMed]
- 28. Tedesco, I.; Carbone, V.; Spagnuolo, C.; Minasi, P.; Russo, GL Identifikatioun a Quantifizéierung vu Flavonoiden aus zwee süd-italienesche Sorten vun Allium cepa L., Tropea (roude Zwiebel) a Montoro (Kupfer Zwiebel), an hir Kapazitéit fir mënschlech Erythrozyten aus oxidativen Stress ze schützen. J. Agric. Food Chem. 2015, 63, 5229-5238. [CrossRef]
- 29. Villano, C.; Esposito, S.; Carucci, F.; Frusciante, L.; Carputo, D.; Aversano, R. High-Throughput Genotyping am Zwiebel weist d'Struktur vun der genetescher Diversitéit an informativen SNPs nëtzlech fir molekulare Zucht. Mol. Zucht. 2019, 39, 5. [CrossRef]
- 30. Mercati, F.; Longo, C.; Poma, D.; Araniti, F.; Lupini, A.; Mammano, MM; Fiore, MC; Abenavoli, MR; Sunseri, F Genetesch Variatioun vun enger italienescher Tomate mat laanger Haltbarkeet (Solanum lycopersicum L.) Kollektioun duerch SSR a morphologesch Uebsteigenschaften. Genet. Ressource. Crop Evol. 2014, 62, 721-732. [CrossRef]
- 31. Gonzalez-Perez, S.; Mallor, C.; Garces-Claver, A.; Merino, F.; Taboada, A.; Rivera, A.; Pomar, F.; Perovic, D.; Silvar, C. Entdeckt genetesch Diversitéit a Qualitéitseigenschaften an enger Sammlung vun Zwiebel (Allium cepa L.) Landrassen aus Nordweste vu Spuenien. Genetik 2015, 47, 885-900. [CrossRef]
- 32. Lotti, C.; Iovieno, P.; Centomani, I.; Marcotrigiano, AR; Fanelli, V.; Mimiola, G.; Summo, C.; Pavan, S.; Ricciardi, L. Genetesch, bio-agronomesch an Ernährungscharakteriséierung vu Kale (Brassica oleracea L. var. acephala) Diversitéit an Apulien, Süditalien. Diversitéit 2018,10, 25. [CrossRef]
- 33. Bardaro, N.; Marcotrigiano, AR; Bracuto, V.; Mazzeo, R.; Ricciardi, F.; Lotti, C.; Pavan, S.; Ricciardi, L. Genetesch Analyse vun Resistenz zu Orobanche crenata (Forsk.) an enger Ierzebulli (Pisum sativum L.) niddereg-strigolacton Linn. J. Planz Pathol. 2016, 98, 671-675.
- 34. Wako, T.; Tsukazaki, H.; Yaguchi, S.; Yamashita, K.; Ito, S.; Shigyo, M. Kartéierung vu quantitativen Trait-Loci fir d'Bolting Zäit am Bunching Zwiebel (Allium fistulosum L.). Euphytica 2016, 209, 537-546. [CrossRef]
- 35. Dhaka, N.; Mukhopadhyay, A.; Paritosh, K.; Gupta, V.; Pental, D.; Pradhan, AK Identifikatioun vun Genic SSRs a Konstruktioun vun enger SSR-baséiert Linkage Kaart an Brassica juncea. Euphytica 2017, 213, 15. [CrossRef]
- 36. Anandhan, S.; Motte, SR; Gopal, J. Evaluatioun vun der Zwiebel Varietéit Identitéit mat SSR Marker. Seed Sci. Technol. 2014, 42, 279-285. [CrossRef]
- 37. Mitrova, K.; Svoboda, P.; Ovesna, J. D'Auswiel an d'Validatioun vun engem Marker-Set fir d'Differenzéierung vun Zwiebelkultivaren aus der Tschechescher Republik. Tschechesch J. Genet. Planzenzucht. 2015, 51, 62-67. [CrossRef]
- 38. Di Rienzo, V.; Miazzi, MM; Fanelli, V.; Sabetta, W.; Montemurro, C. D'Erhaalung an d'Charakteriséierung vun der Apulian Olive Keimplasma Biodiversitéit. Acta Hortic. 2018,1199,1-6. [CrossRef]
- 39. Mallor, C.; Arnedo-Andres, A.; Garces-Claver, A. D'genetesch Diversitéit vu Spuenesch bewäerten Allium cepa Landracen fir Zwiebelzucht mat Mikrosatellitmarker. Sci. Hortic. 2014,170, 24-31. [CrossRef]
- 40. Rivera, A.; Mallor, C.; Garces-Claver, A.; Garcia-Uloa, A.; Pomar, F.; Silvar, C. Assesséiere vun der genetescher Diversitéit an Zwiebel (Allium cepa L.) Landracen aus Nordweste vu Spuenien a Verglach mat der europäescher Verännerlechkeet. NZJ Crop Hortic. 2016, 44, 103-120. [CrossRef]
- 41. De Giovanni, C.; Pavan, S.; Taranto, F.; Di Rienzo, V.; Miazzi, MM; Marcotrigiano, AR; Mangini, G.; Montemurro, C.; Ricciardi, L.; Lotti, C. Genetesch Variatioun vun enger globaler Keimplasmasammlung vu Chickpea (Cicer arietinum L.) dorënner italienesch Bäitrëtter am Risiko vun der genetescher Erosioun. Physiol. Mol. Biol. Planzen 2017, 23, 197-205. [CrossRef]
- 42. Mazzeo, R.; Morgese, A.; Sonnante, G.; Zuluaga, DL; Pavan, S.; Ricciardi, L.; Lotti, C. Genetesch Diversitéit am Broccoli Rabe (Brassica rapa L. subsp. sylvestris (L.) Janch.) aus Süditalien. Sci. Hortic. 2019, 253, 140-146. [CrossRef]
- 43. Jakse, M.; Martin, W.; McCallum, J.; Havey, M. Single Nukleotid polymorphisms, indels, an einfach Sequenz Widderhuelung fir Ënn cultivar Identifikatioun. J. Am. Soc. Hortic. Sci. 2005,130, 912-917. [CrossRef]
- 44. McCallum, J.; Thomson, S.; Pither-Joyce, M.; Kenel, F. Genetesch Diversitéit Analyse an Single-Nukleotid Polymorphismus Marker Entwécklung am kultivéierte Knollen Ënn baséiert op ausgedréckt Sequenz Tag-einfach Sequenz Wiederhol Marker. J. Am. Soc. Hortic. Sci. 2008,133, 810-818. [CrossRef]
- 45. Baldwin, S.; Pither-Joyce, M.; Wright, K.; Chen, L.; McCallum, J. Entwécklung vu robuste genomesche einfache Sequenz Wiederholungsmarker fir Schätzung vun der genetescher Diversitéit bannent a tëscht Knollen Zwiebel. (Allium cepa L.) Populatiounen. Mol. Zucht. 2012, 30, 1401-1411. [CrossRef]
- 46. DeWoody, JA; Honeycutt, RL; Skow, LC Mikrosatellit Markéierer a wäiss Schwanz Hirsch. J. Hered. 1995, 86, 317-319. [CrossRef] [PubMed]
- 47. Khodadadi, M.; Hassanpanah, D. Iranesch Ënn (Allium cepa L.) cultivars Äntwerten op Inzuchtdepressioun. Welt Appl. Sci. J. 2010,11, 426-428.
- 48. Abdou, R.; Bakasso, Y.; Saadou, M.; Baudoin, JP; Hardy, OJ Genetesch Diversitéit vun Niger Zwiebelen (Allium cepa L.) bewäert duerch einfache Sequenzwidderhuelungsmarker (SSR). Acta Hortic. 2016,1143, 77-90. [CrossRef]
- 49. Pavan, S.; Lotti, C.; Marcotrigiano, AR; Mazzeo, R.; Bardaro, N.; Bracuto, V.; Ricciardi, F.; Taranto, F.; D'Agostino, N.; Schiavulli, A.; et al. E markante genetesche Stärekoup a kultivéierte Kichererbëss wéi opgedeckt duerch genombreet Marker Entdeckung a Genotyping. Plant Genom 2017, 2017,10. [CrossRef]
- 50. Pavan, S.; Marcotrigiano, AR; Ciani, E.; Mazzeo, R.; Zonno, V.; Ruggieri, V.; Lotti, C.; Ricciardi, L. Genotyping-duerch-Sequenzéierung vun enger Melon (Cucumis melo L.) Keimplasmasammlung vun engem sekundären Zentrum vun der Diversitéit beliicht Mustere vun der genetescher Variatioun a genomesch Feature vu verschiddene Genpools. BMC Genom. 2017, 18, 59. [CrossRef]
- 51. Di Rienzo, V.; Sion, S.; Taranto, F.; D'Agostino, N.; Montemurro, C.; Fanelli, V.; Sabetta, W.; Boucheffa, S.; Tamendjari, A.; Pasqualone, A.; et al. Genetesch Flux tëscht Olivebevëlkerung am Mëttelmierbecken. Peer J. 2018, 6. [CrossRef]
- 52. Schäfer, LD; McLay, TG Zwee Mikro-Skala Protokoller fir d'Isolatioun vun DNA aus polysaccharide-räich Planz Otemschwieregkeeten. J. Plant Res. 2011,124, 311-314. [CrossRef]
- 53. Doyle, JJ; Doyle, JL Isolatioun vu Planzen DNA aus frëschem Tissu. konzentréieren 1990,12, 13-14.
- 54. Kuhl, JC; Cheung, F.; Qiaoping, Y.; Martin, W.; Zewdie, Y.; McCallum, J.; Katanach, A.; Rutherford, P.; Spull, KC; Jenderek, M.; et al. En eenzegaartege Set vun 11,008 Zwiebel ausgedréckt Sequenz Tags verroden ausgedréckte Sequenz a genomesch Differenzen tëscht de Monocot Uerderen Asparagales a Poales. Planzzell 2004,16, 114-125. [CrossRef]
- 55. Kim, HJ; Lee, HR; Hyun, JY; Lidd, KH; Kim, KH; Kim, JE; Huer, CG; Harn, CH Marker Entwécklung fir Zwiebel genetesch Rengheetstest mat SSR Finder. Koreanesch J. Breed. Sci. 2012, 44, 421-432. [CrossRef]
- 56. Schuelke, M. Eng wirtschaftlech Method fir fluorescent Etikettéierung vun PCR Fragmenter. Nat. Biotechnol. 2000, 18, 233-234. [CrossRef] [PubMed]
- 57. Peakall, R.; Smouse, PE GenAlEx 6.5: Genetesch Analyse an Excel. Populatiounsgenetesch Software fir Léier a Fuerschung: En Update. Bioinformatik 2012, 28, 2537-2539. [CrossRef] [PubMed]
- 58. Kalinowski, ST; Taper, ML; Marshall, TC Iwwerpréiwung wéi de Computerprogramm CERVUS Genotypingsfehler opmécht, erhéicht den Erfolleg bei der Paternitéitsaufgab. Mol. Ecol. 2007,16, 1099-1106. [CrossRef]
- 59. Pritchard, JK; Stephens, M.; Rosenberg, NA; Donnelly, P. Association Mapping an strukturéiert Populatiounen. Am. J. Humm. Genet. 2000, 67, 170-181. [CrossRef]
- 60. Evanno, G.; Regnaut, S.; Goudet, J. D'Zuel vu Stärekéip vun Individuen z'entdecken mat der Software STRUCTURE: Eng Simulatiounsstudie. Mol. Ecol. 2005,14, 2611-2620. [CrossRef]
- 61. Earl, D.; VonHoldt, B. STRUCTURE HARVESTER: Eng Websäit a Programm fir d'STRUCTURE Output ze visualiséieren an d'Evanno Method ëmzesetzen. Conserv. Genet. Ressource. 2011, 4. [CrossRef]
- 62. Takezaki, N.; Nei, M.; Tamura, K. POPTREEW: Webversioun vu POPTREE fir Bevëlkerungsbeem aus Allele Frequenzdaten ze bauen an e puer aner Quantitéiten ze berechnen. Mol. Biol. Evol. 2014, 31, 1622-1624. [CrossRef]
- 63. Kumar, S.; Stecher, G.; Li, M.; Knyaz, C.; Tamura, K. MEGA X. Molekulare Evolutionär Genetik Analyse iwwer Rechenplattformen. Mol. Biol. Evol. 2018, 35, 1547-1549. [CrossRef]